현미경 영상 처리에서의 AI
AI는 정밀 분할, 잡음 제거, 초고해상도, 자동 영상 획득 등 강력한 기능으로 현미경 영상 처리를 혁신하고 있습니다. 이 글에서는 과학 연구에서 필수적인 AI 도구와 최신 동향을 소개합니다.
AI 기술은 영상 획득 최적화와 분석 자동화를 통해 현미경 분야에 혁신을 일으키고 있습니다. 최신 스마트 현미경에서는 AI 모듈이 촬영 매개변수(예: 초점, 조명)를 실시간으로 조정하여 광표백을 최소화하고 신호를 향상시킵니다. 한편, 딥러닝 알고리즘은 복잡한 영상 데이터를 분석해 숨겨진 생물학적 통찰을 추출하고, 유전체학 등 다른 데이터와 연계하기도 합니다.
AI 방법론: 머신러닝과 딥러닝
AI 방법론은 전통적인 머신러닝(ML)부터 최신 딥러닝(DL)까지 다양합니다. 각 접근법은 고유한 강점과 한계를 지닙니다:
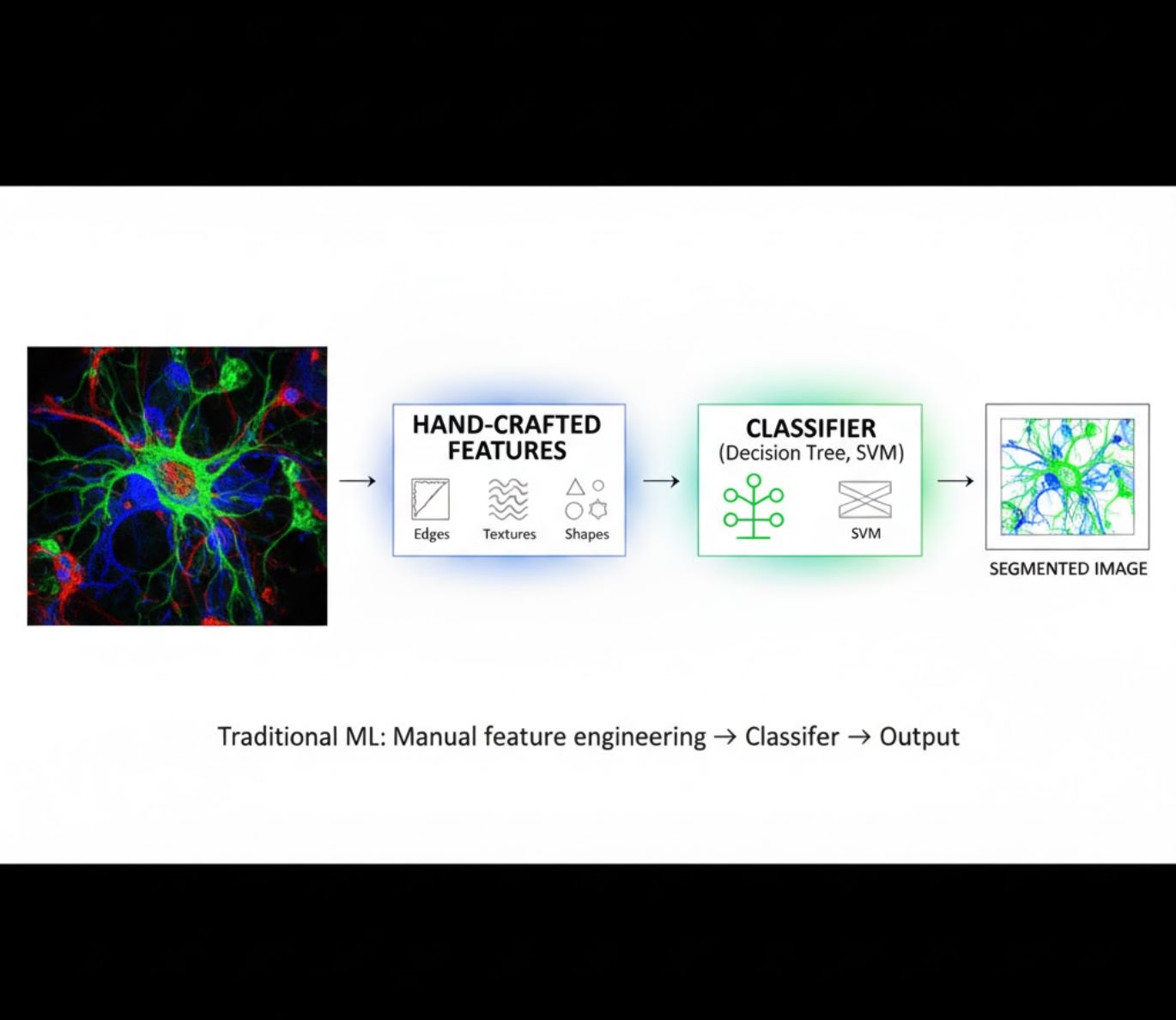
수작업 특징 설계
- 연구자가 직접 영상 특징(모서리, 질감, 형태)을 설계
- 특징을 결정 트리, SVM 등 분류기에 입력
- 학습 속도가 빠름
- 복잡하거나 잡음이 많은 영상에서는 성능 저하
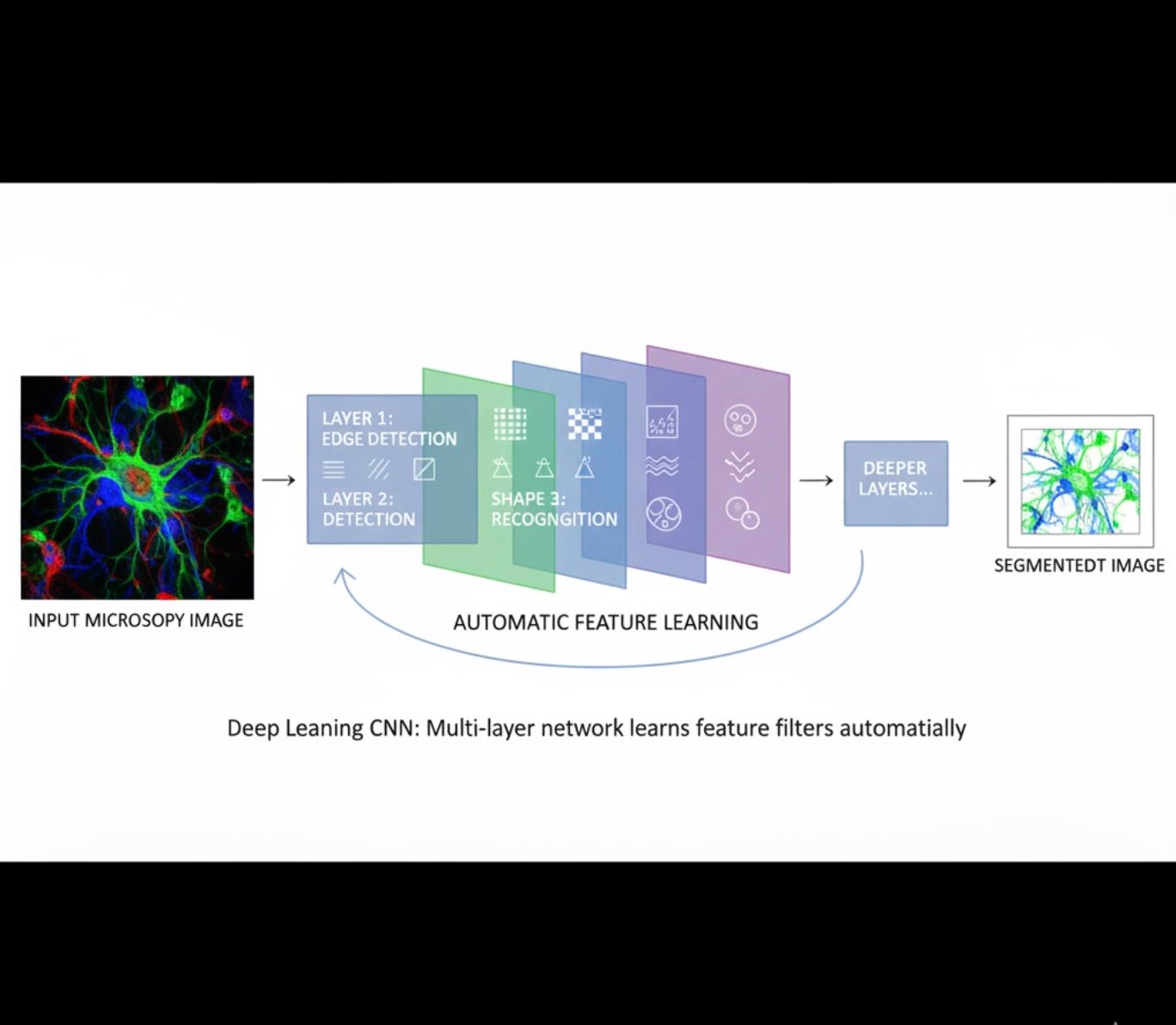
자동 특징 학습
- 다층 신경망(CNN)이 특징을 자동으로 학습
- 원시 픽셀부터 엔드투엔드 학습
- 변화에 훨씬 강건함
- 복잡한 질감과 구조를 신뢰성 있게 포착
CNN 작동 원리: 합성곱 신경망은 현미경 영상을 연속 필터로 처리하며, 초기 층에서는 단순 패턴(모서리)을, 깊은 층에서는 복잡한 구조(세포 형태, 질감)를 학습합니다. 이러한 계층적 학습 덕분에 DL은 강도 변화가 심한 영상에서도 매우 견고합니다.
시각적 비교: ML과 DL 파이프라인
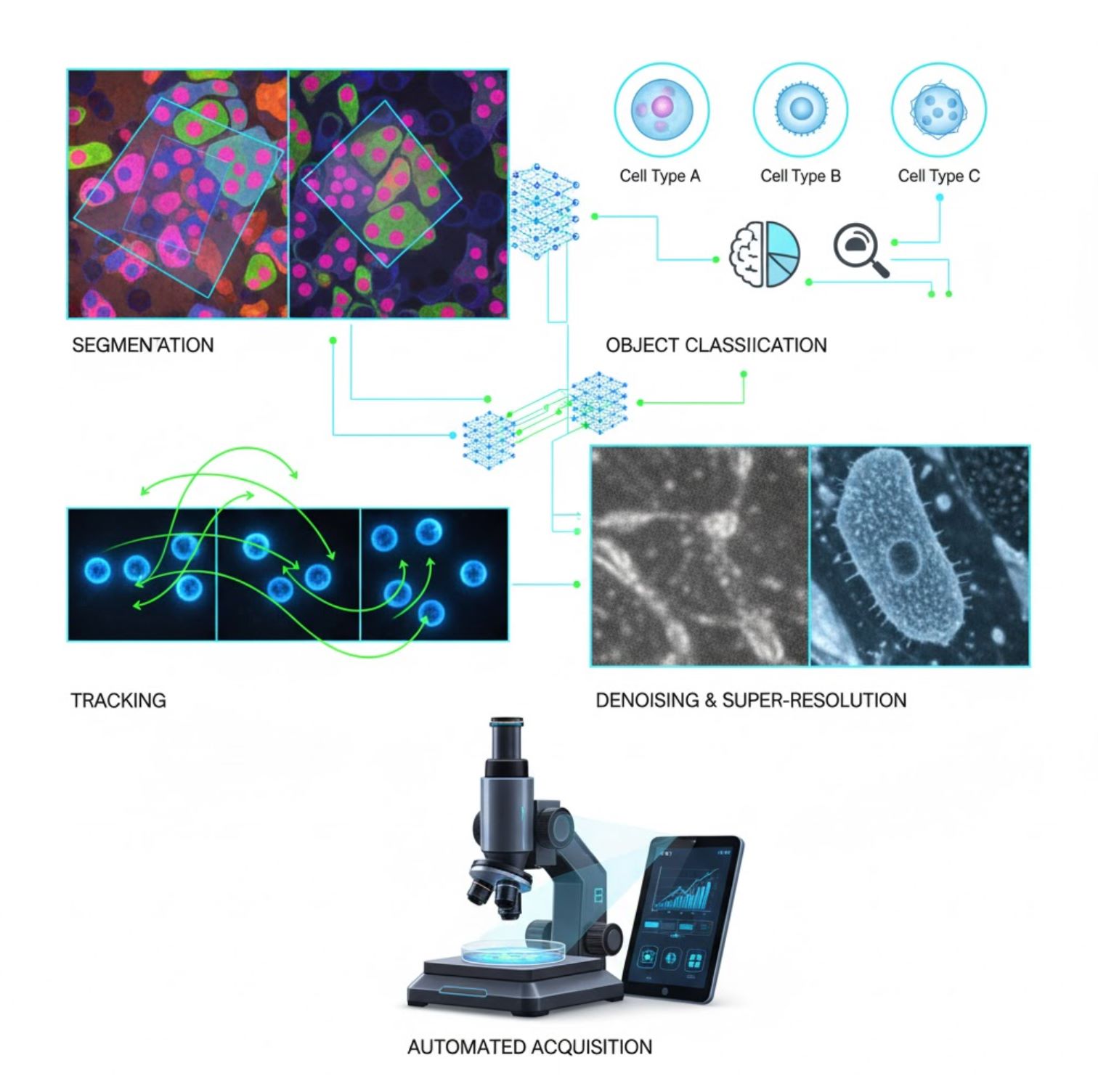
현미경에서의 주요 AI 응용
AI는 현미경 작업 흐름 전반의 다양한 영상 처리 작업에 적용되고 있습니다:
분할
영상을 영역별로 나누기(예: 모든 세포나 핵 식별). U-Net 같은 딥 네트워크가 뛰어납니다.
- 의미론적 분할: 픽셀 단위 클래스 레이블
- 인스턴스 분할: 개별 객체 분리
- 혼잡하거나 어두운 영상에서도 높은 정확도
- μSAM 등 비전 파운데이션 모델이 현미경에 적용 중
객체 분류
분할 후 AI가 각 객체를 높은 정밀도로 분류합니다.
- 세포 유형 식별
- 유사 분열 단계 판별
- 병리학적 지표 탐지
- 수작업으로 정량화하기 어려운 미세 표현형 구분
추적
타임랩스 현미경에서 AI는 프레임 간 세포나 입자를 전례 없는 정확도로 추적합니다.
- 딥러닝이 추적 정확도를 크게 향상
- 움직이는 세포의 신뢰성 있는 분석 가능
- 동적 생물학적 과정 포착
잡음 제거 및 초고해상도
AI 모델은 잡음과 흐림을 제거해 영상 품질을 향상시킵니다.
- 물리 기반 딥 모델이 현미경 광학 특성 학습
- 더 선명하고 인공물 없는 영상 재구성
- 전통적 방법 대비 인공물 감소와 고해상도 구현
자동 획득
AI가 현미경을 실시간으로 제어합니다.
- 실시간 영상 분석으로 지능적 의사결정
- 초점 자동 조정 및 관심 영역 스캔
- 광독성 감소 및 시간 절약
- 고처리량 및 적응형 영상 실험 가능
현미경 영상 처리에 인기 있는 AI 도구
현미경 내 인공지능을 지원하는 다양한 도구들이 풍부한 생태계를 이루고 있습니다. 연구자들은 범용 소프트웨어와 전문화된 소프트웨어를 모두 개발했으며, 그 중 다수는 오픈소스입니다:
Cellpose
| 개발자 | Carsen Stringer와 Marius Pachitariu (MouseLand 연구 그룹) |
| 지원 플랫폼 |
Python(pip/conda 설치) 필요. GUI는 데스크톱에서만 사용 가능. |
| 언어 지원 | 영문 문서 제공; 전 세계 연구실에서 널리 채택됨 |
| 가격 정책 | BSD-3-Clause 라이선스 기반 무료 오픈소스 |
개요
Cellpose는 현미경 이미지용으로 설계된 고급 딥러닝 기반 분할 도구입니다. 범용 알고리즘으로서, 모델 재학습 없이도 다양한 세포 유형(핵, 세포질 등)과 영상 모달리티에서 정확한 분할을 수행합니다. 인간 개입형 기능을 통해 연구자는 결과를 정제하고, 모델을 자신의 데이터에 맞게 조정하며, 2D 및 3D 영상 워크플로우에 적용할 수 있습니다.
주요 기능
맞춤 학습 없이도 다양한 세포 유형, 염색법, 영상 모달리티에 바로 적용 가능.
2D 모델을 재활용하는 "2.5D" 방식을 사용해 전체 3D 스택 지원.
분할 결과를 수동으로 수정하고 맞춤 데이터로 모델을 재학습하여 정확도 향상.
Python API, 명령줄 인터페이스, 그래픽 사용자 인터페이스를 통한 유연한 작업 흐름 지원.
분할 전 영상 품질 향상을 위한 노이즈 제거, 흐림 보정, 업샘플링 기능 제공.
다운로드 또는 접근
기술 배경
Cellpose는 Stringer, Wang, Michaelos, Pachitariu가 발표한 기념비적 연구에서 소개되었으며, 7만 개 이상의 분할된 객체로 구성된 크고 매우 다양한 데이터셋으로 학습되었습니다. 이 다양성 덕분에 모델은 세포 형태, 크기, 현미경 설정 전반에 걸쳐 일반화가 가능해 대부분의 경우 맞춤 학습 필요성을 크게 줄였습니다. 3D 데이터의 경우, Cellpose는 2D 모델을 "2.5D" 방식으로 재활용하여 완전한 3D 주석 학습 데이터 없이도 부피 분할을 수행합니다. Cellpose 2.0은 인간 개입형 재학습을 도입해 사용자가 예측을 수동으로 수정하고 자신의 이미지로 재학습하여 특정 데이터셋에서 성능을 개선할 수 있게 했습니다.
설치 및 설정
conda를 사용해 Python 환경을 설정하세요:
conda create -n cellpose python=3.10환경을 활성화한 후 Cellpose를 설치하세요:
# For GUI support
pip install cellpose[gui]
# For minimal setup (API/CLI only)
pip install cellpose시작하기
GUI 모드
- 다음 명령어로 GUI를 실행하세요:
python -m cellpose - 이미지 파일(
.tif,.png등)을 인터페이스에 드래그 앤 드롭 - 모델 유형 선택(예: 세포질용 "cyto", 핵용 "nuclei")
- 예상 세포 직경을 설정하거나 Cellpose가 자동 보정하도록 설정
- 분할 시작 버튼 클릭 후 결과 확인
Python API 모드
from cellpose import models
# Load model
model = models.Cellpose(model_type='cyto')
# Segment images
masks, flows = model.eval(images, diameter=30)정제 및 재학습
- 마스크 생성 후 GUI에서 수동으로 마스크 병합 또는 삭제하여 분할 수정
- 내장된 학습 기능을 사용해 수정된 예제로 재학습 수행
- 특정 데이터셋에서 모델 성능 향상
3D 데이터 처리
- 다중 Z TIFF 또는 부피 스택 로드
- GUI 또는 API에서
--Zstack플래그를 사용해 3D로 처리 - 더 나은 분할을 위해 스무딩 또는 특수 매개변수를 통해 3D 흐름 정제 가능
제한 사항 및 고려 사항
- 모델 범용성의 한계: 범용 모델이 널리 작동하지만, 매우 특이한 세포 형태나 영상 조건은 재학습이 필요할 수 있음.
- 주석 작업 부담: 인간 개입형 학습은 수동 수정이 필요해 대규모 데이터셋에서는 시간이 많이 소요될 수 있음.
- 설치 복잡성: GUI 설치 시 명령줄 사용, conda 환경 설정, Python 의존성 관리가 필요해 비전문가에게는 다소 어려울 수 있음.
- 데스크톱 전용: Cellpose는 데스크톱 사용을 위해 설계되었으며, Android 또는 iOS 네이티브 앱은 제공되지 않음.
자주 묻는 질문
아니요 — Cellpose는 사전 학습된 범용 모델을 제공하여 대부분의 경우 재학습 없이도 잘 작동합니다. 다만, 특수하거나 비정형 데이터에 대해 최적의 결과를 원한다면 인간 개입형 기능을 사용해 주석 처리 및 재학습이 가능합니다.
네 — 2D 모델을 재활용하는 "2.5D" 방식을 지원하며, GUI나 API를 통해 부피 스택을 처리할 수 있습니다.
GPU는 대용량 또는 3D 데이터셋에서 추론 및 학습 속도를 높이기 위해 강력히 권장되지만, CPU만으로도 작동은 가능하나 성능이 느립니다.
GUI에서 예상 세포 직경을 수동으로 설정하거나 Cellpose가 자동으로 보정하도록 할 수 있습니다. 분할이 최적이 아닐 경우 결과를 정제하고 재학습할 수 있습니다.
네 — 최신 버전(Cellpose 3)에는 분할 전 영상 품질 향상을 위한 노이즈 제거, 흐림 보정, 업샘플링 기능이 포함되어 있습니다.
StarDist
| 개발자 | 우베 슈미트, 마틴 바이거트, 콜먼 브로드더스, 진 마이어스 |
| 지원 플랫폼 |
|
| 언어 지원 | 주로 영어로 된 문서와 커뮤니티를 갖춘 오픈소스 프로젝트 |
| 가격 모델 | 무료 및 오픈 소스. BSD-3-Clause 라이선스 적용 |
개요
StarDist는 현미경 이미지에서 인스턴스 분할을 위한 딥러닝 도구입니다. 각 객체(예: 세포 핵)를 2D의 스타-컨벡스 다각형 또는 3D의 다면체로 표현하여, 밀집하거나 겹친 객체를 정확하게 탐지하고 분리할 수 있습니다. 견고한 아키텍처 덕분에 형광 현미경, 조직병리학 및 기타 생물영상 분석 분야에서 자동 세포 및 핵 분할에 널리 사용됩니다.
주요 특징
스타-컨벡스 다각형(2D) 및 다면체(3D)를 사용하여 신뢰성 높은 객체 탐지와 매우 정확한 인스턴스 분할을 제공합니다.
2D 이미지와 3D 볼륨 데이터 모두를 위한 전용 모델로 포괄적인 현미경 분석을 지원합니다.
형광 핵, H&E 염색 조직 등 일반적인 영상 시나리오에 바로 사용할 수 있는 모델을 제공합니다.
단일 분할 실행에서 탐지된 객체를 서로 다른 클래스(예: 다양한 세포 유형)로 분류할 수 있습니다.
ImageJ/Fiji, QuPath, napari와 원활하게 통합되어 GUI 기반 워크플로우를 제공합니다.
정밀도, 재현율, F1 점수, 파노프틱 품질 등 포괄적인 인스턴스 분할 평가 기능을 포함합니다.
기술 배경
StarDist는 2018년 MICCAI 논문에서 처음 소개되었으며, 고정된 광선을 따라 방사 거리와 객체 확률을 예측하여 스타-컨벡스 형태를 정확히 재구성하는 혁신적인 방법을 제시했습니다. 이 접근법은 기존 픽셀 기반 또는 경계 상자 방식으로 분리하기 어려운 밀접한 객체를 신뢰성 있게 분할합니다.
최근에는 조직병리학 이미지로 확장되어 핵 분할뿐 아니라 탐지된 객체의 다중 클래스 분류도 가능해졌으며, CoNIC(대장 핵 식별 및 계수) 챌린지 등에서 최고 성능을 기록했습니다.
다운로드 또는 접근
설치 및 설정
StarDist 사용을 위해 TensorFlow(버전 1.x 또는 2.x)를 먼저 설치하세요.
pip를 사용하여 StarDist 파이썬 패키지를 설치하세요:
pip install stardistnapari용:
pip install stardist-napariQuPath용: StarDist 확장 파일(.jar)을 QuPath에 드래그하여 설치하세요.
ImageJ/Fiji용: 내장 플러그인 관리자 또는 플러그인 메뉴를 통해 수동 설치가 가능합니다.
분할 실행
사전 학습된 모델을 불러오고, 이미지를 정규화한 후 예측을 실행하세요:
from stardist.models import StarDist2D
model = StarDist2D.from_pretrained('2D_versatile_fluo')
labels, details = model.predict_instances(image)napari에서 이미지를 열고 StarDist 플러그인을 선택한 후, 사전 학습 또는 사용자 정의 모델을 선택하여 GUI에서 직접 예측을 실행하세요.
플러그인 메뉴에서 StarDist를 사용하여 직관적인 인터페이스로 이미지 스택에 모델을 적용하세요.
확장 설치 후 QuPath의 스크립팅 콘솔 또는 그래픽 인터페이스를 통해 조직병리학 분석용 StarDist 탐지를 실행하세요.
학습 및 미세 조정
각 객체가 고유하게 라벨링된 정답 레이블 이미지를 만드세요. LabKit, QuPath, Fiji 같은 주석 도구를 사용해 데이터셋을 준비할 수 있습니다.
StarDist 파이썬 API를 사용하여 새 모델을 학습하거나, 사용자 주석 데이터로 기존 모델을 미세 조정하세요.
후처리 옵션
- 중복 후보 형태를 제거하기 위해 비최대 억제(NMS)를 적용하세요
- 비스타-컨벡스 형태 병합을 위해 StarDist OPP(객체 후처리)를 사용하세요
제한 사항 및 고려 사항
- 스타-컨벡스 가정은 매우 비컨벡스하거나 불규칙한 형태를 완벽히 모델링하지 못할 수 있습니다
- 설치 복잡성: 확장 빌드를 위해 호환되는 C++ 컴파일러가 필요합니다
- GPU 가속은 호환되는 TensorFlow, CUDA, cuDNN 버전에 따라 달라집니다
- 일부 사용자는 Java 설정 문제로 ImageJ 플러그인 실행에 어려움을 겪는다고 보고합니다
자주 묻는 질문
StarDist는 형광, 밝은장, 조직병리학(H&E 등) 등 다양한 이미지 유형에서 작동하며, 유연한 사전 학습 모델과 다양한 영상 모달리티에 적응할 수 있습니다.
네, StarDist는 3D 볼륨 데이터에 대해 스타-컨벡스 다면체를 사용한 3D 인스턴스 분할을 지원하여 2D 기능을 확장합니다.
반드시 그렇지는 않습니다. 사전 학습된 모델이 바로 잘 작동하는 경우가 많지만, 특수하거나 새로운 데이터의 경우 직접 주석을 달고 맞춤형 모델을 학습하면 정확도가 크게 향상됩니다.
StarDist는 napari, ImageJ/Fiji, QuPath와 통합되어 GUI에서 코딩 없이 분할을 실행할 수 있으며, 고급 워크플로우를 위한 직접 파이썬 API 사용도 지원합니다.
StarDist는 정밀도, 재현율, F1 점수, 파노프틱 품질 등 일반적인 인스턴스 분할 지표를 계산하는 내장 기능을 제공하여 분할 성능을 평가할 수 있습니다.
SAM
적용 정보
| 개발자 | Meta AI Research (FAIR) |
| 지원 기기 |
|
| 언어 및 제공 | 전 세계에서 사용 가능한 오픈소스 기초 모델; 문서는 영어로 제공 |
| 가격 | 무료 — Meta 라이선스 하에 GitHub 및 MIB 통합을 통해 오픈소스 제공 |
일반 개요
SAM(Segment Anything Model)은 Meta에서 개발한 강력한 AI 기초 모델로, 이미지 내 거의 모든 객체를 대화형 및 자동으로 분할할 수 있습니다. 점, 경계 상자, 대략적인 마스크와 같은 프롬프트를 사용하여 작업별 재학습 없이 분할 마스크를 생성합니다. 현미경 연구 분야에서 SAM의 유연성은 세포 분할, 세포 소기관 탐지, 조직병리학 분석에 적용되어 프롬프트 기반의 범용 분할 도구가 필요한 연구자들에게 확장 가능한 솔루션을 제공합니다.
상세 소개
원래 Meta에서 11백만 장의 이미지와 10억 개 이상의 마스크로 학습된 SAM은 새로운 도메인에 대해 "제로샷" 성능을 제공하는 프롬프트 기반 기초 모델로 설계되었습니다. 의료 영상 연구에서는 전체 슬라이드 병리 분할, 종양 탐지, 세포 핵 식별에 대해 평가되었습니다. 그러나 세포 핵과 같이 밀집된 인스턴스에서는 성능이 혼재되어 있으며, 20회 클릭 또는 박스와 같은 광범위한 프롬프트에도 불구하고 복잡한 현미경 이미지에서 제로샷 분할이 어려울 수 있습니다.
이 한계를 극복하기 위해 도메인별 적응이 등장했습니다:
- SAMCell — 다양한 세포 유형에 대해 실험별 재학습 없이 강력한 제로샷 분할을 위해 대규모 현미경 데이터셋으로 미세 조정됨
- μSAM — 17,000개 이상의 수동 주석 현미경 이미지로 재학습되어 작은 세포 구조에 대한 정확도 향상
주요 기능
점, 박스, 마스크를 사용한 유연한 상호작용으로 정밀 제어 가능.
새로운 이미지 도메인에 대해 미세 조정 없이 분할 수행.
소수 샷 또는 프롬프트 기반 재학습을 통해 현미경 및 조직병리학에 적응 가능.
Microscopy Image Browser(MIB)에서 3D 및 보간 분할 지원 가능.
IDCC-SAM은 면역세포화학에서 수동 주석 없이 자동 세포 계수를 가능하게 함.
다운로드 또는 접근
사용자 가이드
- Microscopy Image Browser를 열고 SAM 분할 패널로 이동
- Python 인터프리터를 구성하고 SAM-1 또는 SAM-2 모델 선택
- GPU 가속을 위해 실행 환경에서 "cuda" 선택(최적 성능 권장)
- 포인트 프롬프트: 객체를 클릭하여 양성 시드 정의; Shift + 클릭으로 확장, Ctrl + 클릭으로 음성 시드 지정
- 3D 스택: 대화형 3D 모드 사용—한 슬라이스 클릭 후 Shift-스크롤로 슬라이스 간 시드 보간
- 조정 모드: 필요에 따라 마스크 교체, 추가, 제거 또는 새 레이어 생성
- MIB의 SAM-2 패널에서 "Automatic everything" 옵션을 사용하여 영역 내 모든 가시 객체 분할
- 분할 후 마스크 검토 및 필요 시 수정
- 프롬프트 기반 미세 조정 파이프라인(예: "All-in-SAM")을 사용하여 희소 사용자 프롬프트로 픽셀 수준 주석 생성
- 세포 계수에는 SAM을 제로샷 파이프라인과 후처리로 사용하는 IDCC-SAM 적용
- 고정밀 세포 분할을 위해 현미경 세포 이미지로 미세 조정된 SAMCell 사용
제한 사항 및 고려사항
- 도메인 튜닝 없이는 밀집되거나 겹치는 구조에서 제로샷 성능 불안정
- 분할 품질은 프롬프트 설계 및 전략에 크게 좌우됨
- GPU 강력 권장; CPU 추론은 매우 느림
- 초고해상도 전체 슬라이드 이미지 및 다중 스케일 조직 구조에서 어려움
- 현미경용 SAM 미세 조정 또는 적응에는 머신러닝 전문 지식 필요할 수 있음
자주 묻는 질문
네—SAMCell과 같은 적응을 통해 현미경 데이터셋에 대해 SAM을 미세 조정하여 세포 분할 작업에 특화시켰습니다.
항상 그런 것은 아닙니다. IDCC-SAM을 사용하면 수동 주석 없이 제로샷 세포 계수가 가능합니다.
프롬프트 기반 미세 조정(예: "All-in-SAM") 또는 17,000개 이상의 주석 현미경 이미지로 학습된 μSAM과 같은 사전 학습된 현미경 버전을 사용하세요.
CPU에서도 가능하지만, 실용적인 추론 속도와 실시간 대화형 분할을 위해 GPU를 강력히 권장합니다.
네—MIB의 SAM-2 통합은 슬라이스 간 시드 보간을 통한 3D 분할을 지원하여 부피 분석이 가능합니다.
AxonDeepSeg
| 개발자 | 몬트리올 폴리테크닉 및 몬트리올 대학교 NeuroPoly 연구실 |
| 지원 플랫폼 |
|
| 언어 | 영문 문서; 전 세계에서 사용되는 오픈소스 도구 |
| 가격 | 무료 및 오픈소스 |
개요
AxonDeepSeg는 현미경 이미지에서 축삭과 미엘린을 자동으로 분할하는 AI 기반 도구입니다. 합성곱 신경망을 활용해 TEM, SEM, 밝은장 현미경 등 다양한 영상 기법에서 정확한 3클래스 분할(축삭, 미엘린, 배경)을 제공합니다. 축삭 직경, g-비율, 미엘린 두께 등 형태계측 측정을 자동화하여 신경과학 연구에서 정량 분석을 간소화하고 수작업 주석 시간을 크게 줄이며 재현성을 향상시킵니다.
주요 기능
TEM, SEM, 밝은장 현미경 영상에 최적화된 즉시 사용 가능한 모델.
현미경 이미지에서 축삭, 미엘린, 배경 영역을 정밀하게 분류.
축삭 직경, g-비율, 미엘린 두께, 밀도 지표를 자동으로 계산.
Napari GUI 통합으로 분할 마스크를 수동으로 정밀 조정 가능.
대규모 신경 조직 분석을 위한 맞춤형 파이프라인에 원활히 통합.
재현성과 신뢰할 수 있는 분할 결과를 보장하는 종합 테스트 스크립트.
기술 세부사항
NeuroPoly 연구실에서 개발한 AxonDeepSeg는 딥러닝을 활용해 신경과학 응용 분야에 고정밀 분할을 제공합니다. 다양한 현미경 기법별 사전학습 모델을 제공하여 영상 기법 전반에 걸쳐 활용 가능합니다. Napari와 통합되어 분할 마스크의 대화형 수정을 지원하며, 까다로운 데이터셋에서 정확도를 높입니다. AxonDeepSeg는 주요 형태계측 지표를 계산하여 신경 조직 구조 및 병리 연구의 고처리량 분석을 지원합니다. 파이썬 기반 프레임워크로 대규모 축삭 및 미엘린 형태 분석 맞춤 파이프라인에 통합할 수 있습니다.
다운로드 또는 접근
설치 및 설정
Python 3.8 이상이 설치되어 있는지 확인한 후, pip를 사용해 AxonDeepSeg와 Napari를 설치하세요:
pip install axondeepseg napari제공된 테스트 스크립트를 실행하여 모든 구성 요소가 올바르게 설치되고 작동하는지 확인하세요.
TEM, SEM 또는 밝은장 현미경 이미지를 Napari 또는 파이썬 환경에 불러오세요.
영상 기법에 맞는 사전학습 모델을 선택하고 분할을 실행하여 축삭 및 미엘린 마스크를 생성하세요.
축삭 직경, g-비율, 밀도, 미엘린 두께 등 형태계측 지표를 자동으로 계산하고 결과를 CSV 형식으로 내보내세요.
필요한 경우 Napari GUI를 사용해 분할 마스크를 수동으로 조정하고 병합 또는 삭제하여 정확도를 높이세요.
중요 고려사항
- 새롭거나 학습되지 않은 영상 기법에서는 성능 저하 가능
- 복잡하거나 까다로운 영역은 수동 수정 필요할 수 있음
- 대용량 데이터셋 처리 시 GPU 권장; 소규모 분석은 CPU도 지원
자주 묻는 질문
AxonDeepSeg는 TEM(투과전자현미경), SEM(주사전자현미경), 밝은장 현미경을 지원하며, 각 기법에 최적화된 사전학습 모델을 제공합니다.
네, AxonDeepSeg는 완전 무료이자 오픈소스로, 학술 및 상업적 용도로 모두 사용 가능합니다.
네, AxonDeepSeg는 분할된 이미지에서 축삭 직경, g-비율, 미엘린 두께, 밀도 지표를 자동으로 계산합니다.
대용량 데이터셋의 빠른 분할을 위해 GPU 사용을 권장하지만, 소규모 분석은 CPU에서도 지원됩니다.
네, Napari GUI 통합으로 까다로운 영역에서 분할 마스크를 대화형으로 수정하고 정밀하게 다듬을 수 있습니다.
Ilastik
| 개발자 | 유럽 분자생물학 연구소(EMBL) Ilastik 팀 및 관련 학술 파트너 |
| 지원 플랫폼 |
|
| 언어 | 영어 |
| 가격 | 무료 및 오픈소스 |
개요
Ilastik은 현미경 데이터의 대화형 이미지 분할, 분류 및 분석을 위한 강력한 AI 기반 도구입니다. 랜덤 포레스트 분류기와 같은 머신러닝 기법을 사용하여 연구자들이 픽셀을 분할하고, 객체를 분류하며, 시간에 따른 세포 추적과 2D 및 3D 데이터셋에서 밀도 계수를 수행할 수 있게 합니다. 직관적인 인터페이스와 실시간 피드백 덕분에 프로그래밍 전문 지식이 없는 과학자들도 쉽게 접근할 수 있으며, 세포 생물학, 신경과학, 생의학 영상 분야에서 널리 사용되고 있습니다.
주요 기능
대표 영역에 주석을 달면 즉시 분할 결과를 실시간으로 확인할 수 있습니다.
형태학적 및 강도 특징에 기반하여 분할된 구조를 분류합니다.
2D 및 3D 시계열 현미경 실험에서 세포 이동과 분열을 추적합니다.
개별 객체를 명시적으로 분할하지 않고도 혼잡한 영역의 개체 수를 정량화합니다.
직관적인 상호작용으로 복잡한 3D 볼륨을 반자동으로 분할합니다.
헤드리스 명령줄 모드를 사용하여 여러 이미지를 자동으로 처리합니다.
다운로드
시작 가이드
공식 웹사이트에서 운영체제에 맞는 Ilastik을 다운로드하세요. 패키지에는 필요한 모든 Python 종속성이 포함되어 있으니 플랫폼별 설치 지침을 따르십시오.
Ilastik을 열고 분석 워크플로우를 선택하세요: 픽셀 분류, 객체 분류, 추적 또는 밀도 계수. 다중 채널, 3D 또는 시계열 이미지 데이터셋을 불러올 수 있습니다.
이미지에서 대표 픽셀이나 객체 몇 개에 라벨을 지정하세요. Ilastik의 랜덤 포레스트 분류기가 이 주석을 학습하여 전체 데이터셋에 자동으로 라벨을 예측합니다.
학습된 모델을 적용하여 전체 데이터셋을 분할하거나 분류하세요. 결과를 라벨 이미지, 확률 맵 또는 정량적 표 형식으로 내보내 후속 분석 및 시각화에 활용할 수 있습니다.
Ilastik의 헤드리스 모드를 사용하여 수동 개입 없이 여러 이미지를 자동으로 처리할 수 있으며, 대규모 분석 파이프라인에 적합합니다.
제한 사항 및 고려 사항
- 대화형 라벨링은 매우 큰 데이터셋에서 시간이 많이 소요될 수 있습니다
- 정확도는 사용자 주석의 품질과 대표성에 따라 달라집니다
- 메모리 요구량 — 매우 고해상도 또는 수 기가바이트 데이터셋은 상당한 RAM이 필요할 수 있습니다
- 복잡한 데이터 — 랜덤 포레스트 분류기는 변동성이 크거나 복잡한 영상 데이터에서 딥 뉴럴 네트워크보다 성능이 떨어질 수 있습니다
자주 묻는 질문
네, Ilastik은 3D 볼륨과 시계열 실험을 완벽히 지원하여 여러 시점에 걸친 분할, 추적 및 정량 분석이 가능합니다.
네, Ilastik은 완전 무료이자 오픈소스로, 라이선스 제한 없이 모든 사용자가 이용할 수 있습니다.
아니요, Ilastik은 직관적인 그래픽 인터페이스와 실시간 피드백을 제공하여 프로그래밍 전문 지식 없이도 연구자들이 쉽게 사용할 수 있습니다. 고급 사용자는 명령줄 배치 처리도 활용할 수 있습니다.
네, 전용 추적 워크플로우를 통해 2D 및 3D 시계열 데이터셋에서 세포 이동과 분열을 자동 계통 추적과 함께 분석할 수 있습니다.
분할 결과는 라벨 이미지, 확률 맵 또는 정량적 표 형식으로 내보낼 수 있어 후속 분석 도구 및 시각화 소프트웨어와 원활하게 연동됩니다.
이 도구들은 초보자부터 전문가까지 다양하게 활용할 수 있습니다. 많은 도구가 무료 오픈소스로, 연구 커뮤니티 내에서 재현 가능하고 공유 가능한 AI 워크플로우를 지원합니다.
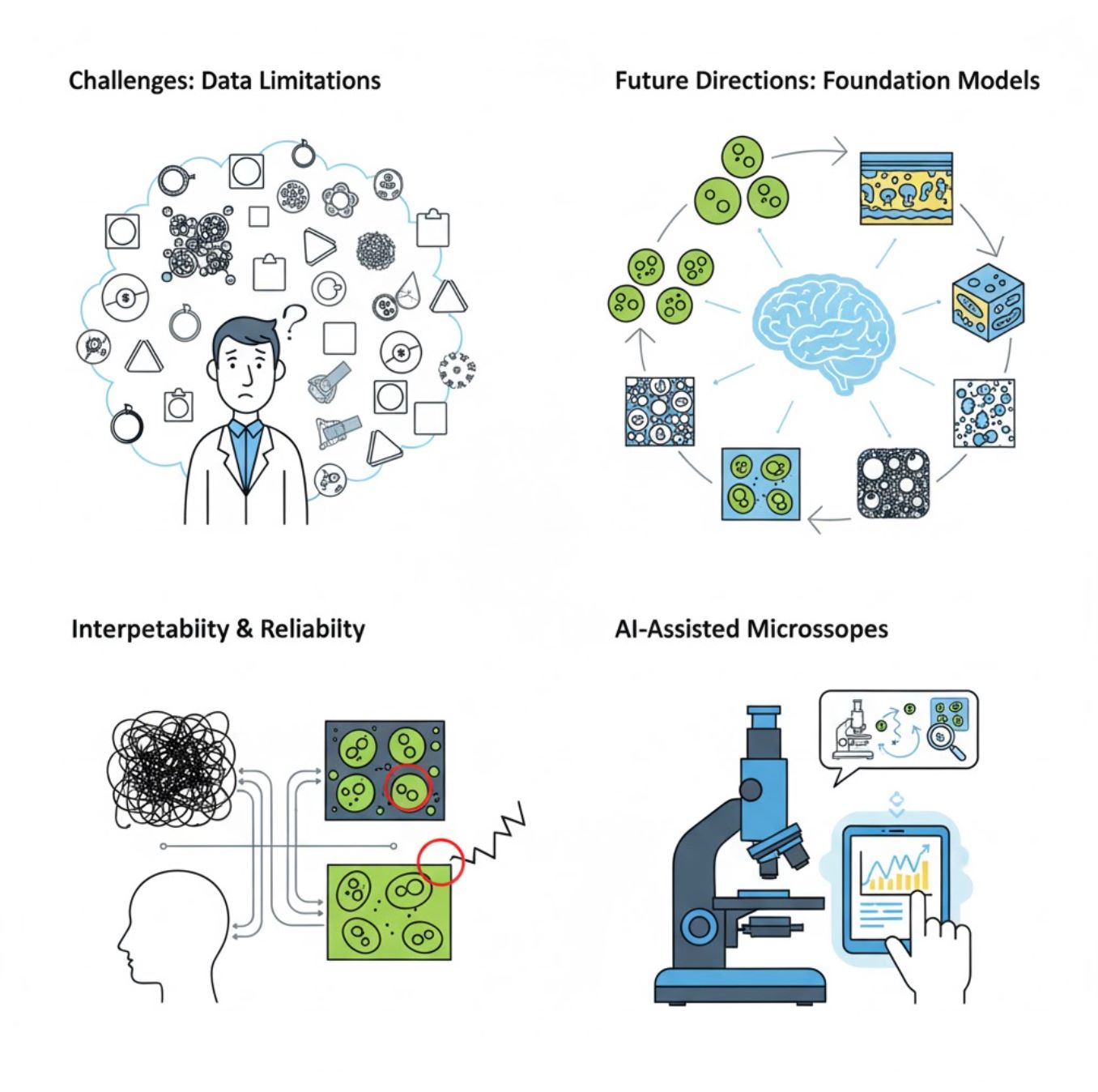
과제와 미래 방향
현재 과제
신흥 동향
비전 파운데이션 모델
차세대 AI 시스템은 특정 작업별 학습 필요성을 줄일 전망입니다.
- SAM, CLIP 기반 모델 등
- 하나의 AI가 다양한 현미경 작업 처리
- 더 빠른 배포와 적응
AI 지원 현미경
완전 자율적이고 지능적인 현미경 시스템이 현실화되고 있습니다.
- 대규모 언어 모델(LLM)을 통한 자연어 제어
- 완전 자동화된 피드백 루프
- 첨단 현미경 접근성 민주화
주요 요점 정리
- AI는 정확도와 자동화를 개선하며 현미경 영상 처리를 빠르게 변화시키고 있습니다
- 딥러닝은 복잡하고 변화가 심한 현미경 영상에서 전통적 머신러닝보다 뛰어납니다
- CNN은 원시 픽셀부터 계층적 특징을 자동 학습해 견고한 분석을 제공합니다
- 주요 응용 분야는 분할, 분류, 추적, 잡음 제거, 자동 획득입니다
- 성공은 양질의 데이터와 전문가의 신중한 검증에 달려 있습니다
- 비전 파운데이션 모델과 AI 지원 현미경이 이 분야의 미래를 이끌 것입니다
지속적인 발전과 커뮤니티 노력(오픈소스 도구, 공유 데이터셋)을 통해 AI는 점점 더 현미경의 '눈' 역할을 하며 과학자들이 보이지 않는 것을 볼 수 있도록 도울 것입니다.







No comments yet. Be the first to comment!