בינה מלאכותית בעיבוד תמונות מיקרוסקופ
הבינה המלאכותית משנה את תחום עיבוד תמונות המיקרוסקופ עם יכולות מתקדמות כגון סגמנטציה מדויקת, הפחתת רעש, רזולוציה-על ורכישת תמונות אוטומטית. מאמר זה מדגיש כלים חיוניים של בינה מלאכותית ומגמות מתפתחות במחקר המדעי.
טכניקות בינה מלאכותית מהפכניות במיקרוסקופיה על ידי אופטימיזציה של רכישת תמונות ו-אוטומציה של ניתוח. במיקרוסקופים חכמים מודרניים, מודולי בינה מלאכותית יכולים לכוונן פרמטרים של הדמיה בזמן אמת (למשל, מיקוד, תאורה) כדי למזער דהייה פוטוכימית ולשפר את האות. במקביל, אלגוריתמים של למידה עמוקה יכולים לסנן נתוני תמונה מורכבים כדי לחלץ תובנות ביולוגיות נסתרות ואפילו לקשר תמונות לנתונים אחרים (למשל, גנומיקה).
שיטות בינה מלאכותית: למידת מכונה מול למידה עמוקה
שיטות בינה מלאכותית נעות מלמידת מכונה קלאסית (ML) ועד למידה עמוקה מודרנית (DL). לכל גישה יש חוזקות ומגבלות מובחנות:
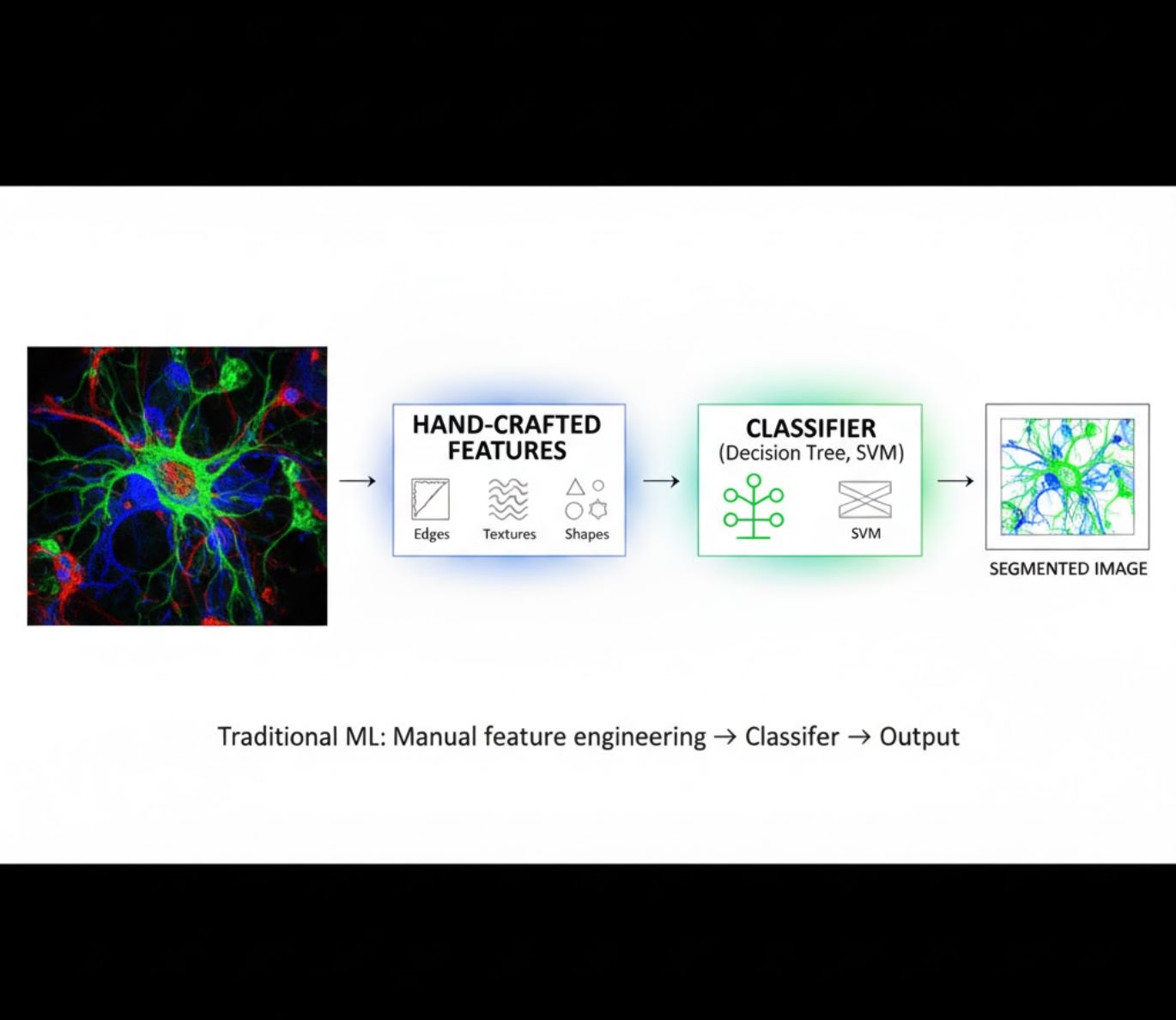
תכונות מעוצבות ידנית
- חוקרים מעצבים תכונות תמונה (קצוות, מרקמים, צורות) באופן ידני
- התכונות מוזנות לממיינים (עצים החלטיים, SVM)
- מהיר לאימון
- מתקשה עם תמונות מורכבות או רועשות
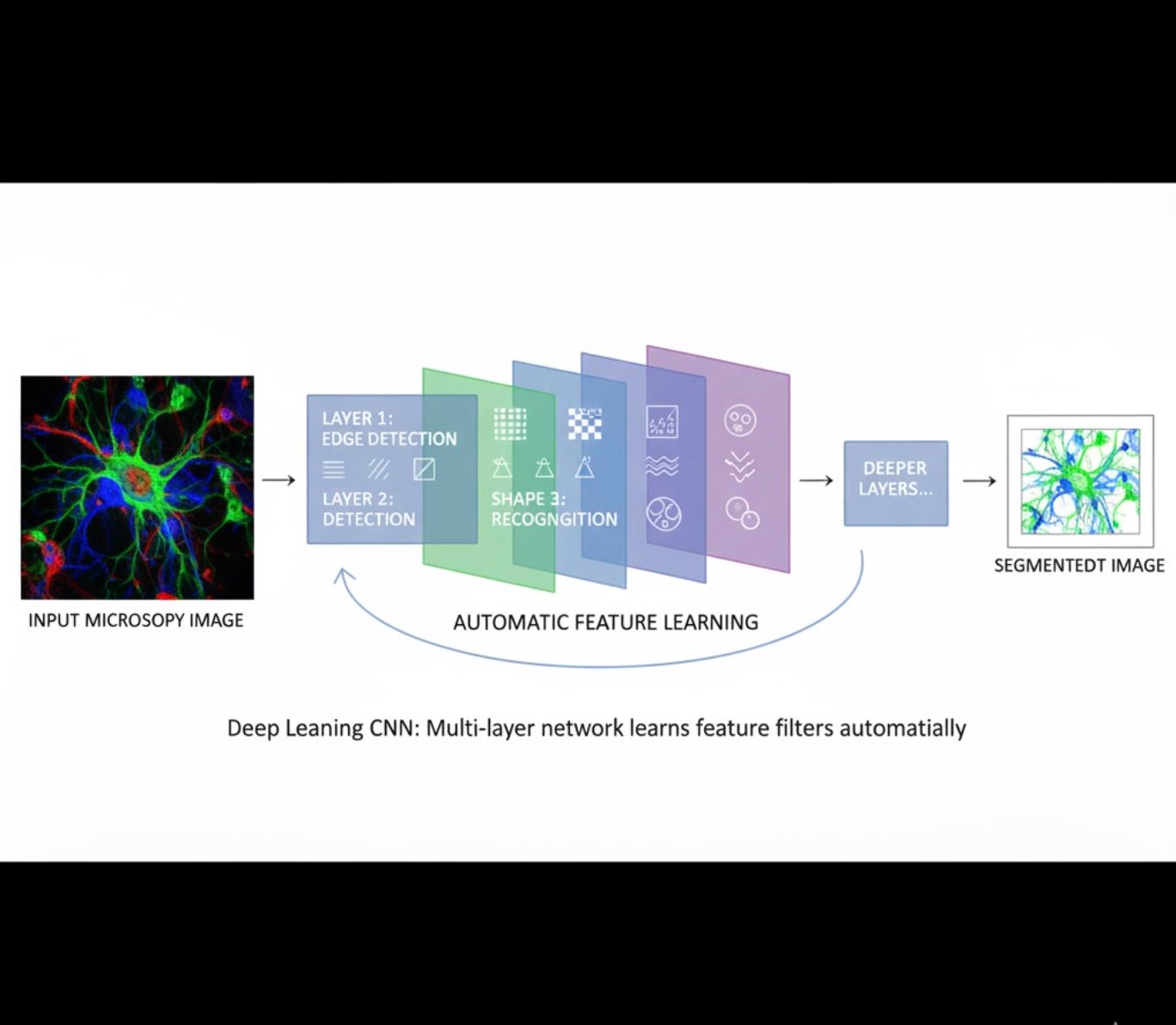
למידת תכונות אוטומטית
- רשתות עצביות רב-שכבתיות (CNN) לומדות תכונות באופן אוטומטי
- למידה מקצה לקצה מפיקסלים גולמיים
- עמידות גבוהה יותר לשינויים
- לוכדת מרקמים ומבנים מורכבים באופן אמין
איך CNN פועלות: רשתות עצביות קונבולוציוניות מיישמות מסננים עוקבים על תמונות מיקרוסקופ, לומדות לזהות דפוסים פשוטים (קצוות) בשכבות הראשונות ומבנים מורכבים (צורות תאים, מרקמים) בשכבות העמוקות. למידה היררכית זו הופכת את ה-DL לעמידה במיוחד גם כאשר פרופילי האינטנסיביות משתנים משמעותית.
השוואה ויזואלית: צינורות ML מול DL
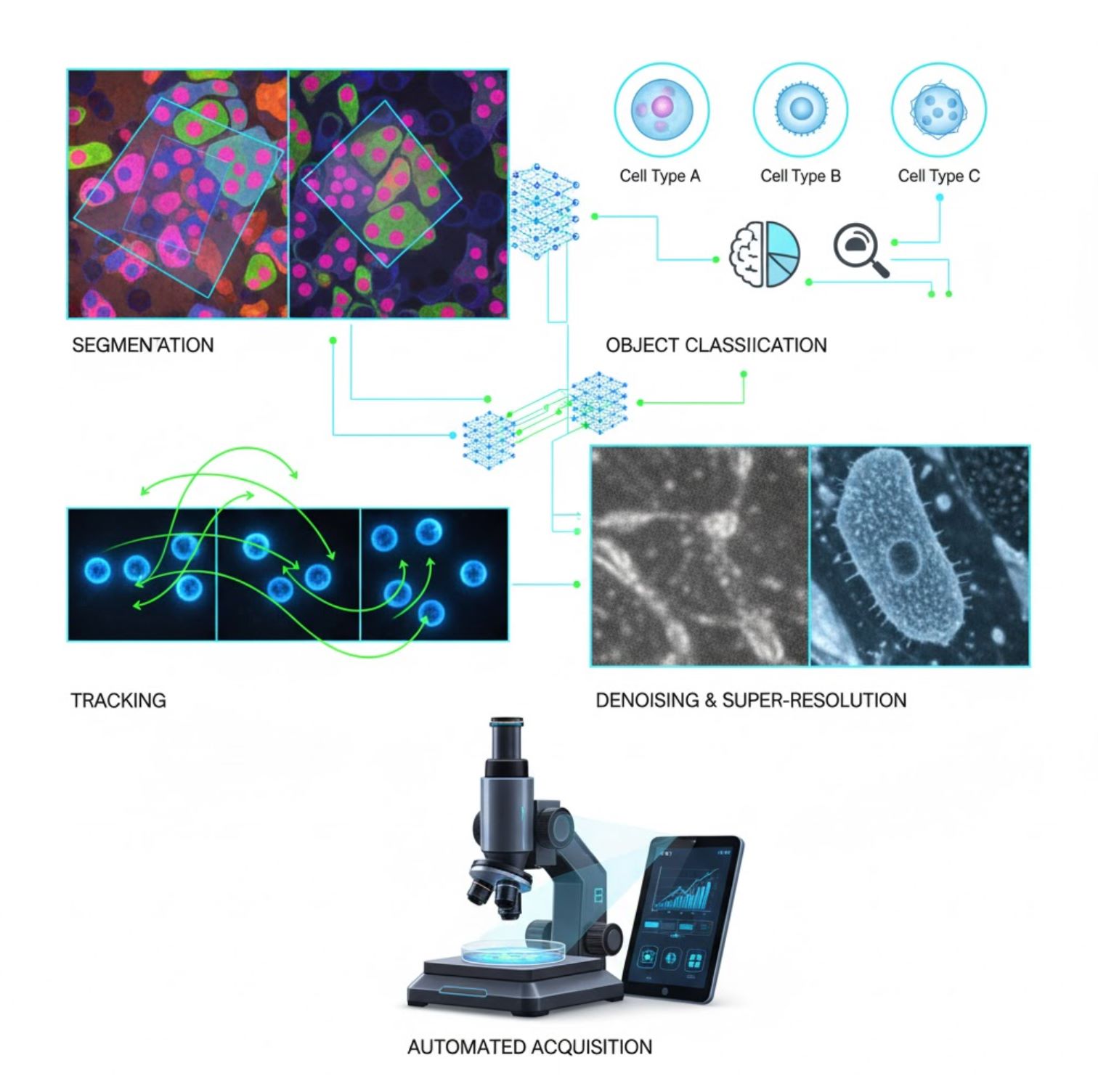
יישומים מרכזיים של בינה מלאכותית במיקרוסקופיה
בינה מלאכותית משולבת כיום במשימות רבות של עיבוד תמונה לאורך תהליך המיקרוסקופיה:
סגמנטציה
חלוקת תמונות לאזורים (למשל, זיהוי כל תא או גרעין). רשתות עמוקות כמו U-Net מצטיינות במשימה זו.
- סגמנטציה סמנטית: תוויות מחלקה לכל פיקסל
- סגמנטציה אינסטנסית: הפרדת עצמים בודדים
- דיוק גבוה בתמונות צפופות או עמומות
- מודלים בסיסיים של ראייה (כגון μSAM) מותאמים כעת למיקרוסקופיה
סיווג עצמים
לאחר הסגמנטציה, הבינה המלאכותית מסווגת כל עצם בדיוק גבוה.
- זיהוי סוגי תאים
- קביעת שלב מיטוטי
- זיהוי אינדיקטורים פתולוגיים
- מבדילה פנוטיפים עדינים שקשה לכמת ידנית
מעקב
במיקרוסקופיה בזמן אמת, הבינה המלאכותית עוקבת אחרי תאים או חלקיקים בין פריימים בדיוק חסר תקדים.
- למידה עמוקה משפרת משמעותית את דיוק המעקב
- מאפשרת ניתוח אמין של תאים נעים
- לוכדת תהליכים ביולוגיים דינמיים
הפחתת רעש ורזולוציה-על
מודלים של בינה מלאכותית משפרים את איכות התמונה על ידי הסרת רעש וטשטוש.
- מודלים עמוקים המודעים לפיזיקה לומדים את אופטיקת המיקרוסקופ
- משחזרים תמונות חדות וללא ארטיפקטים
- רזולוציה גבוהה יותר עם פחות ארטיפקטים לעומת שיטות מסורתיות
רכישה אוטומטית
הבינה המלאכותית מנווטת את המיקרוסקופ בזמן אמת.
- מנתחת תמונות חיות לקבלת החלטות חכמות
- מתאימה אוטומטית מיקוד וסורקת אזורי עניין
- מפחיתה פוטוטוקסיות וחוסכת זמן
- מאפשרת ניסויים בהדמיה בקצב גבוה ובאופן אדפטיבי
כלים פופולריים של בינה מלאכותית בעיבוד תמונות מיקרוסקופ
מערכת אקולוגית עשירה של כלים תומכת ב-AI במיקרוסקופיה. החוקרים פיתחו תוכנות כלליות וממוקדות, רבות מהן קוד פתוח:
Cellpose
| מפתח | Carsen Stringer ו-Marius Pachitariu (קבוצת המחקר MouseLand) |
| פלטפורמות נתמכות |
דורש Python (התקנה באמצעות pip/conda). ממשק גרפי זמין רק בשולחן עבודה. |
| תמיכת שפה | תיעוד באנגלית; מאומץ ברחבי העולם במעבדות מחקר |
| מודל תמחור | חינמי וקוד פתוח תחת רישיון BSD-3-Clause |
סקירה כללית
Cellpose הוא כלי מתקדם לחלוקת תאים מבוסס למידה עמוקה, המיועד לתמונות מיקרוסקופ. כאלגוריתם כללי, הוא מחלק במדויק סוגי תאים מגוונים (גרעינים, ציטופלזמה וכו') במודאליות הדמיה שונות ללא צורך באימון מחודש של המודל. עם יכולות מעורבות משתמש, חוקרים יכולים לשפר תוצאות, להתאים את המודל לנתונים שלהם, ולהפעיל את המערכת על זרימות עבודה דו-ממדיות ותלת-ממדיות.
תכונות עיקריות
פועל מיידית עבור מגוון רחב של סוגי תאים, צבעים ומודאליות הדמיה ללא צורך באימון מותאם.
תומך בערימות תלת-ממד מלאות באמצעות גישת "2.5D" שמשתמשת במודלים דו-ממדיים לנתונים וולומטריים.
תקן ידנית תוצאות חלוקה ואמן מחדש את המודל על הנתונים המותאמים שלך לשיפור הדיוק.
גישה דרך API בפייתון, ממשק שורת פקודה, או ממשק גרפי לעבודה גמישה.
יכולות להפחתת רעש, הסרת טשטוש, והגדלת רזולוציה לשיפור איכות התמונה לפני החלוקה.
הורדה או גישה
רקע טכני
Cellpose הוצג במחקר מפתח של Stringer, Wang, Michaelos ו-Pachitariu, ואומן על מאגר נתונים גדול ומגוון מאוד המכיל מעל 70,000 עצמים מחולקים. גיוון זה מאפשר למודל להכליל בין צורות, גדלים והגדרות מיקרוסקופ שונות, ומפחית משמעותית את הצורך באימון מותאם ברוב המקרים. עבור נתונים תלת-ממדיים, Cellpose משתמש במודל הדו-ממדי שלו בצורה "2.5D", ומונע את הצורך בנתוני אימון מתויגים תלת-ממדיים מלאים תוך שמירה על חלוקה וולומטרית. בגרסה 2.0 הוצגה אפשרות אימון מחודש עם מעורבות משתמש, המאפשרת תיקון ידני של תחזיות ואימון מחודש על תמונות אישיות לשיפור ביצועים במאגרים ספציפיים.
התקנה והגדרה
הקמת סביבה בפייתון באמצעות conda:
conda create -n cellpose python=3.10הפעל את הסביבה והתקן את Cellpose:
# For GUI support
pip install cellpose[gui]
# For minimal setup (API/CLI only)
pip install cellposeהתחלה מהירה
מצב GUI
- הפעל את הממשק הגרפי באמצעות הפקודה:
python -m cellpose - גרור ושחרר קבצי תמונה (
.tif,.pngוכו') לממשק - בחר סוג מודל (למשל "cyto" לציטופלזמה או "nuclei" לגרעינים)
- הגדר קוטר תא משוער או אפשר ל-Cellpose לכייל אוטומטית
- לחץ להתחלת החלוקה וצפה בתוצאות
מצב API בפייתון
from cellpose import models
# Load model
model = models.Cellpose(model_type='cyto')
# Segment images
masks, flows = model.eval(images, diameter=30)שיפור ואימון מחודש
- לאחר יצירת המסכות, תקן את החלוקה בממשק הגרפי על ידי מיזוג או מחיקת מסכות ידנית
- השתמש בפונקציות האימון המובנות לאימון מחודש על הדוגמאות המתוקנות
- שיפור ביצועי המודל על מאגר הנתונים הספציפי שלך
עיבוד נתונים תלת-ממדיים
- טען קובץ TIFF רב-מישורי או ערימת ווליום
- השתמש בדגל
--Zstackבממשק הגרפי או ב-API לעיבוד כתלת-ממד - אופציונלי: שפר זרימות תלת-ממד באמצעות החלקה או פרמטרים מיוחדים לחלוקה טובה יותר
מגבלות ושיקולים
- פשרת כלליות המודל: למרות שהמודל הכללי פועל ברוחב, צורות תאים או תנאי הדמיה יוצאי דופן עשויים לדרוש אימון מחודש.
- מאמץ תיוג: אימון עם מעורבות משתמש דורש תיקונים ידניים, שיכולים להיות גוזלי זמן במאגרים גדולים.
- מורכבות התקנה: התקנת הממשק הגרפי עשויה לדרוש שימוש בשורת הפקודה, סביבות conda, וניהול תלות בפייתון — לא תמיד פשוט למשתמשים לא טכניים.
- רק שולחן עבודה: Cellpose מיועד לשימוש במחשב שולחני; אין אפליקציות מקוריות לאנדרואיד או iOS.
שאלות נפוצות
לא — Cellpose מספק מודלים כלליים מאומנים מראש שעובדים טוב ללא אימון מחודש. עם זאת, לתוצאות מיטביות על נתונים מיוחדים או יוצאי דופן, ניתן לתייג ולאמן מחדש באמצעות תכונות מעורבות המשתמש.
כן — הוא תומך בתלת-ממד על ידי שימוש חוזר במודל הדו-ממדי שלו (הנקרא "2.5D"), וניתן להריץ ערימות וולומטריות דרך הממשק הגרפי או ה-API.
מומלץ מאוד להשתמש ב-GPU לאינפרנס ואימון מהירים יותר, במיוחד במאגרים גדולים או תלת-ממדיים, אך ניתן להפעיל את Cellpose גם על מחשבים עם CPU בלבד עם ביצועים איטיים יותר.
בממשק הגרפי, הגדר את קוטר התא המשוער ידנית או אפשר ל-Cellpose לכייל אוטומטית. ניתן לשפר תוצאות ולאמן מחדש אם החלוקה אינה מיטבית.
כן — גרסאות חדשות (Cellpose 3) כוללות מודלים לשחזור תמונות להפחתת רעש, הסרת טשטוש, והגדלת רזולוציה לשיפור איכות החלוקה לפני העיבוד.
StarDist
| מפתח | אווה שמידט, מרטין וייגרט, קולמן ברודוס, וג'ין מאיירס |
| פלטפורמות נתמכות |
|
| תמיכה בשפות | פרויקט קוד פתוח עם תיעוד וקהילה בעיקר באנגלית |
| מודל תמחור | חינמי וקוד פתוח. מורשה תחת BSD-3-Clause |
סקירה כללית
StarDist היא כלי למידה עמוקה לסגמנטציה של מופעים בתמונות מיקרוסקופיות. היא מייצגת כל אובייקט (כגון גרעיני תאים) כפוליגון כוכב-קמור ב-2D או כפוליהדרון ב-3D, ומאפשרת זיהוי והפרדה מדויקת של אובייקטים צפופים או חופפים. עם הארכיטקטורה החזקה שלה, StarDist משמשת נרחב לסגמנטציה אוטומטית של תאים וגרעינים במיקרוסקופיית פלואורסצנציה, היסטופתולוגיה ויישומי ניתוח ביואימג' נוספים.
תכונות מרכזיות
סגמנטציה מדויקת מאוד של מופעים באמצעות פוליגונים כוכב-קמורים (2D) ופוליהדרונים (3D) לזיהוי אמין של אובייקטים.
מודלים ייעודיים לתמונות דו-ממדיות ולנתונים וולומטריים תלת-ממדיים לניתוח מיקרוסקופי מקיף.
מודלים מוכנים לשימוש לגרעיני פלואורסצנציה, היסטולוגיה בצביעה H&E ותרחישי הדמיה נפוצים נוספים.
סיווג אובייקטים שזוהו למחלקות מובחנות (למשל, סוגי תאים שונים) בהרצה אחת של הסגמנטציה.
שילוב חלק עם ImageJ/Fiji, QuPath ו-napari עבור זרימות עבודה מבוססות ממשק משתמש גרפי נגישות.
הערכת סגמנטציה מקיפה הכוללת דיוק, שליפה, ציון F1 ואיכות פנופטית.
רקע טכני
הוצג לראשונה במאמר MICCAI 2018, החידוש המרכזי של StarDist הוא חיזוי מרחקים רדיאליים לאורך קרניים קבועות בשילוב עם הסתברות אובייקט לכל פיקסל, המאפשר שיחזור מדויק של צורות כוכב-קמורות. גישה זו מסגמנטת באופן אמין אובייקטים צמודים שקשה להפרידם בשיטות מסורתיות מבוססות פיקסלים או תיבות גבול.
פיתוחים אחרונים הרחיבו את StarDist לתמונות היסטופתולוגיה, המאפשרים לא רק סגמנטציה של גרעינים אלא גם סיווג רב-מעמדי של האובייקטים שזוהו. השיטה השיגה ביצועים מובילים באתגרים כגון אתגר CoNIC (זיהוי וספירת גרעיני המעי הגס).
הורדה או גישה
התקנה והגדרה
התקן את TensorFlow (גרסה 1.x או 2.x) כתנאי מוקדם ל-StarDist.
השתמש ב-pip להתקנת חבילת StarDist בפייתון:
pip install stardistל-napari:
pip install stardist-napariל-QuPath: התקן את ההרחבה של StarDist על ידי גרירת קובץ .jar לתוך QuPath.
ל-ImageJ/Fiji: השתמש במנהל התוספים המובנה או בהתקנה ידנית דרך תפריט התוספים.
הרצת סגמנטציה
טען מודל מאומן מראש, נרמל את התמונה שלך, והרץ חיזוי:
from stardist.models import StarDist2D
model = StarDist2D.from_pretrained('2D_versatile_fluo')
labels, details = model.predict_instances(image)פתח את התמונה שלך ב-napari, בחר בתוסף StarDist, בחר מודל מאומן מראש או מותאם, והרץ חיזוי ישירות מהממשק הגרפי.
השתמש בתוסף StarDist מתפריט התוספים כדי להחיל מודל על ערמת התמונות שלך עם ממשק אינטואיטיבי.
לאחר התקנת ההרחבה, הרץ זיהוי StarDist דרך קונסולת הסקריפטים או הממשק הגרפי של QuPath לניתוח היסטופתולוגיה.
אימון וכיוונון
צור תמונות תיוג אמת קרקע שבהן כל אובייקט מתויג באופן ייחודי. השתמש בכלי הערות כמו LabKit, QuPath או Fiji להכנת מערך הנתונים שלך.
השתמש ב-API של StarDist בפייתון לאימון מודל חדש או לכיוונון מודל קיים עם הנתונים המותאמים שלך.
אפשרויות עיבוד לאחר
- הפעלת דיכוי מקסימום לא-מקסימלי (NMS) להסרת צורות מועמדות מיותרות
- השתמש ב-StarDist OPP (עיבוד לאחר אובייקט) למיזוג מסכות לצורות לא כוכב-קמורות
מגבלות ושיקולים
- הנחת כוכב-קמור עשויה שלא להתאים לצורות מאוד לא קמורות או לא סדירות
- מורכבות התקנה: התקנות מותאמות דורשות מהדר C++ תואם לבניית הרחבות
- האצת GPU תלויה בגרסאות תואמות של TensorFlow, CUDA ו-cuDNN
- חלק מהמשתמשים מדווחים על בעיות בהרצת תוסף ImageJ עקב הגדרות Java
שאלות נפוצות
StarDist עובדת עם מגוון סוגי תמונות כולל פלואורסצנציה, שדה בהיר והיסטופתולוגיה (למשל, H&E), בזכות המודלים הגמישים המאומנים מראש והיכולת להסתגל למודאליות הדמיה שונות.
כן — StarDist תומכת בסגמנטציה של מופעים תלת-ממדיים באמצעות פוליהדרונים כוכב-קמורים לנתונים וולומטריים, ומרחיבה את היכולות מ-2D לניתוח תלת-ממדי מלא.
לא בהכרח. קיימים מודלים מאומנים מראש שעובדים טוב ישירות. עם זאת, עבור נתונים מיוחדים או חדשים, תיוג ואימון מודלים מותאמים משפרים משמעותית את הדיוק.
StarDist משתלבת עם napari, ImageJ/Fiji ו-QuPath, ומאפשרת הרצת סגמנטציה מממשק משתמש גרפי ללא קידוד. כמו כן, תומכת בשימוש ישיר ב-API של Python לזרימות עבודה מתקדמות.
StarDist מספקת פונקציות מובנות לחישוב מדדי סגמנטציה נפוצים כולל דיוק, שליפה, ציון F1 ואיכות פנופטית להערכת ביצועי הסגמנטציה.
SAM
מידע על היישום
| מפתח | Meta AI Research (FAIR) |
| מכשירים נתמכים |
|
| שפה וזמינות | מודל יסוד בקוד פתוח זמין ברחבי העולם; תיעוד באנגלית |
| תמחור | חינמי — בקוד פתוח תחת רישיון Meta דרך GitHub ואינטגרציה ב-MIB |
סקירה כללית
SAM (Segment Anything Model) הוא מודל יסוד חזק מבוסס בינה מלאכותית שפותח על ידי Meta ומאפשר חלוקה אינטראקטיבית ואוטומטית של כמעט כל עצם בתמונות. באמצעות פרומפטים כגון נקודות, תיבות תחום או מסכות גסות, SAM מייצר מסכות חלוקה ללא צורך באימון חוזר ספציפי למשימה. במחקר מיקרוסקופי, הגמישות של SAM הותאמה לחלוקת תאים, זיהוי אברונים וניתוח היסטופתולוגיה, ומציעה פתרון מדרגי לחוקרים הזקוקים לכלי חלוקה כללי הניתן להפעלה באמצעות פרומפט.
הקדמה מפורטת
באופן מקורי, SAM אומן על ידי Meta על מעל 1 מיליארד מסכות ב-11 מיליון תמונות, ועוצב כמודל יסוד הניתן להפעלה באמצעות פרומפט עם ביצועי "זירו-שוט" על תחומים חדשים. במחקר הדמיה רפואית, SAM הוערך לחלוקת פתולוגיה על שקופיות שלמות, זיהוי גידולים וזיהוי גרעיני תאים. עם זאת, ביצועיו במקרים של עצמים צפופים — כגון גרעיני תאים — מעורבים: גם עם פרומפטים נרחבים (למשל, 20 לחיצות או תיבות), חלוקה במצב זירו-שוט עלולה להתקשות בתמונות מיקרוסקופיות מורכבות.
כדי להתמודד עם מגבלה זו, פותחו התאמות ספציפיות לתחום:
- SAMCell — כוונון מחדש על מערכי נתוני מיקרוסקופיה גדולים לחלוקה חזקה במצב זירו-שוט על סוגי תאים מגוונים ללא צורך באימון חוזר לכל ניסוי
- μSAM — אומן מחדש על מעל 17,000 תמונות מיקרוסקופיה מתויגות ידנית לשיפור הדיוק במבנים תאיים קטנים
תכונות מרכזיות
אינטראקציה גמישה באמצעות נקודות, תיבות ומסכות לשליטה מדויקת.
מבצע חלוקה ללא כוונון מחדש על תחומי תמונה חדשים.
ניתן להתאמה למיקרוסקופיה והיסטופתולוגיה באמצעות אימון חוזר מועט או מבוסס פרומפט.
זמין ב-Microscopy Image Browser (MIB) עם תמיכה בחלוקה תלת-ממדית ומאומצת.
IDCC-SAM מאפשר ספירת תאים אוטומטית באימונוציטוכימיה ללא תיוג ידני.
הורדה או גישה
מדריך למשתמש
- פתח את Microscopy Image Browser ונווט ללוח החלוקה של SAM
- הגדר את מפרש הפייתון ובחר בין דגמי SAM-1 או SAM-2
- להאצת GPU, בחר "cuda" בסביבת ההרצה (מומלץ לביצועים מיטביים)
- פרומפטי נקודה: לחץ על עצם כדי להגדיר נקודת זרע חיובית; השתמש ב-Shift + לחיצה להרחבה ו-Ctrl + לחיצה לנקודות זרע שליליות
- ערימות תלת-ממד: השתמש במצב אינטראקטיבי תלת-ממדי — לחץ על פרוסה אחת, גלול עם Shift, ואינטרפולציה של נקודות זרע בין פרוסות
- מצב התאמה: החלף, הוסף, הפחת מסכות, או צור שכבה חדשה לפי הצורך
- השתמש באפשרות "הכל אוטומטי" בלוח SAM-2 של MIB לחלוקה של כל העצמים הנראים באזור
- סקור ותקן מסכות לאחר החלוקה לפי הצורך
- השתמש בצינורות כוונון מחדש מבוססי פרומפט (למשל, "All-in-SAM") ליצירת תיוגים ברמת פיקסל מפרומפטים דלילים של המשתמש
- לספירת תאים, השתמש ב-IDCC-SAM, המשתמש ב-SAM בצינור זירו-שוט עם עיבוד לאחר מכן
- לחלוקה מדויקת של תאים, השתמש ב-SAMCell, שעבר כוונון מחדש על תמונות מיקרוסקופיה של תאים
מגבלות ושיקולים
- ביצועי זירו-שוט לא עקביים במבנים צפופים או חופפים ללא כוונון תחומי
- איכות החלוקה תלויה מאוד בעיצוב ואסטרטגיית הפרומפט
- מומלץ בחום GPU; ביצועי CPU איטיים מאוד
- מתקשה עם תמונות שקופיות ברזולוציה גבוהה מאוד ומבני רקמה ברב-קנה מידה
- כוונון מחדש או התאמת SAM למיקרוסקופיה עשויים לדרוש מיומנות בלמידת מכונה
שאלות נפוצות
כן — באמצעות התאמות כמו SAMCell, שמכוונן מחדש את SAM על מערכי נתוני מיקרוסקופיה במיוחד למשימות חלוקת תאים.
לא תמיד. עם IDCC-SAM, ניתן לבצע ספירת תאים במצב זירו-שוט ללא תיוגים ידניים.
השתמש בכוונון מחדש מבוסס פרומפט (למשל, "All-in-SAM") או בגרסאות מיקרוסקופיה מאומנות מראש כמו μSAM, שאומן על מעל 17,000 תמונות מיקרוסקופיה מתויגות.
אמנם אפשרי על CPU, אך מומלץ מאוד GPU למהירות ביצוע מעשית וחלוקה אינטראקטיבית בזמן אמת.
כן — האינטגרציה של SAM-2 ב-MIB תומכת בחלוקה תלת-ממדית עם אינטרפולציית נקודות זרע בין פרוסות לניתוח וולומטרי.
AxonDeepSeg
| מפתח | מעבדת NeuroPoly בפוליטכניק מונטריאול ואוניברסיטת מונטריאול |
| פלטפורמות נתמכות |
|
| שפה | תיעוד באנגלית; כלי קוד פתוח בשימוש עולמי |
| תמחור | חינמי וקוד פתוח |
סקירה כללית
AxonDeepSeg הוא כלי מבוסס בינה מלאכותית לסגמנטציה אוטומטית של אקסונים ומיאלין בתמונות מיקרוסקופיה. באמצעות רשתות עצביות קונבולוציוניות, הוא מספק סגמנטציה מדויקת בשלוש קטגוריות (אקסון, מיאלין, רקע) במגוון מודאליות דימות כולל TEM, SEM ומיקרוסקופיה בשדה בהיר. על ידי אוטומציה של מדידות מורפומטריות כגון קוטר אקסון, יחס g ועובי מיאלין, AxonDeepSeg מפשט ניתוח כמותי במחקרי מדעי המוח, ומפחית משמעותית את זמן הסימון הידני ומשפר את החזרות.
תכונות מרכזיות
מודלים מוכנים לשימוש מותאמים למודאליות מיקרוסקופיה TEM, SEM ושדה בהיר.
סיווג מדויק של אזורי אקסון, מיאלין ורקע בתמונות מיקרוסקופיה.
חישוב אוטומטי של קוטר אקסון, יחס g, עובי מיאלין ומדדי צפיפות.
שילוב עם ממשק Napari מאפשר שיפור ידני של מסכות הסגמנטציה לדיוק גבוה יותר.
משתלבת בצורה חלקה בצינורות עבודה מותאמים לניתוח רחב היקף של רקמת עצב.
סקריפטים מקיפים לבדיקות מבטיחים חזרתיות ותוצאות סגמנטציה אמינות.
פרטים טכניים
פותח במעבדת NeuroPoly, AxonDeepSeg מנצל למידה עמוקה לסגמנטציה מדויקת ליישומים במדעי המוח. מודלים מאומנים מראש זמינים למודאליות מיקרוסקופיה שונות, ומבטיחים גמישות בטכניקות דימות. הכלי משתלב עם Napari, ומאפשר תיקונים אינטראקטיביים של מסכות הסגמנטציה, מה שמשפר את הדיוק במערכי נתונים מאתגרים. AxonDeepSeg מחשב מדדים מורפומטריים מרכזיים, ותומך במחקרים בקנה מידה גדול של מבנה רקמת עצב ופאתולוגיה. המסגרת מבוססת הפייתון מאפשרת אינטגרציה בצינורות עבודה מותאמים לניתוח מורפולוגיה של אקסון ומיאלין.
הורדה או גישה
התקנה והגדרה
ודאו ש-Python 3.8 או גרסה מאוחרת יותר מותקנת, ואז התקינו את AxonDeepSeg ו-Napari באמצעות pip:
pip install axondeepseg napariהריצו את סקריפטי הבדיקה המסופקים כדי לוודא שכל הרכיבים מותקנים ופועלים כראוי.
ייבאו תמונות מיקרוסקופיה (TEM, SEM או שדה בהיר) ל-Napari או לסביבת הפייתון שלכם.
בחרו את המודל המאומן המתאים למודאליות הדימות שלכם והריצו סגמנטציה ליצירת מסכות אקסון ומיאלין.
חישוב אוטומטי של מדידות מורפומטריות כולל קוטר אקסון, יחס g, צפיפות ועובי מיאלין, ולאחר מכן ייצוא התוצאות בפורמט CSV.
השתמשו בממשק Napari כדי לכוונן ידנית את מסכות הסגמנטציה במידת הצורך, למיזוג או מחיקה לשיפור הדיוק.
שיקולים חשובים
- הביצועים עשויים לרדת במודאליות דימות חדשות או לא מאומנות
- ייתכן ויידרשו תיקונים ידניים באזורים מאתגרים או מורכבים
- מומלץ להשתמש ב-GPU לעיבוד מהיר של מערכי נתונים גדולים; עיבוד ב-CPU נתמך גם כן
שאלות נפוצות
AxonDeepSeg תומך ב-TEM (מיקרוסקופ אלקטרונים טרנסמיסיבי), SEM (מיקרוסקופ אלקטרונים סורק) ומיקרוסקופיה בשדה בהיר עם מודלים מאומנים מראש מותאמים לכל מודאליות.
כן, AxonDeepSeg הוא חינמי לחלוטין וקוד פתוח, זמין לשימוש אקדמי ומסחרי.
כן, AxonDeepSeg מחשב אוטומטית קוטר אקסון, יחס g, עובי מיאלין ומדדי צפיפות מתמונות שסומנו.
מומלץ להשתמש ב-GPU לסגמנטציה מהירה של מערכי נתונים גדולים, אך עיבוד ב-CPU נתמך גם לניתוחים קטנים יותר.
כן, שילוב עם ממשק Napari מאפשר תיקונים אינטראקטיביים ושיפור ידני של מסכות הסגמנטציה לדיוק גבוה יותר באזורים מאתגרים.
Ilastik
| מפתח | צוות Ilastik במעבדת הביולוגיה המולקולרית האירופית (EMBL) ושותפים אקדמיים נלווים |
| פלטפורמות נתמכות |
|
| שפה | אנגלית |
| תמחור | חינמית וקוד פתוח |
סקירה כללית
Ilastik היא כלי חזק מונחה בינה מלאכותית לסגמנטציה אינטראקטיבית, סיווג וניתוח נתוני מיקרוסקופיה. באמצעות טכניקות למידת מכונה כמו מסווגי Random Forest, היא מאפשרת לחוקרים לסווג פיקסלים, לסווג עצמים, לעקוב אחר תאים לאורך זמן ולבצע ספירת צפיפות במערכי נתונים דו-ממדיים ותלת-ממדיים. עם ממשק אינטואיטיבי ומשוב בזמן אמת, Ilastik נגישה למדענים ללא ידע בתכנות ומאומצת נרחבת בתחומי ביולוגיית התאים, מדעי המוח ודימות רפואי.
תכונות עיקריות
משוב בזמן אמת בעת סימון אזורים מייצגים לתוצאות סגמנטציה מיידיות.
מיון מבנים שסומנו על פי תכונות מורפולוגיות ועוצמתיות.
מעקב אחר תנועת תאים וחלוקתם בניסויי מיקרוסקופיה טיים-לפס דו-ממדיים ותלת-ממדיים.
כימות אזורים צפופים ללא סגמנטציה מפורשת של עצמים בודדים.
סגמנטציה חצי-אוטומטית לנפחים תלת-ממדיים מורכבים עם אינטראקציה אינטואיטיבית.
עיבוד אוטומטי של תמונות מרובות במצב שורת פקודה ללא ממשק גרפי.
הורדה
מדריך התחלה מהירה
הורד את Ilastik למערכת ההפעלה שלך מהאתר הרשמי. החבילה כוללת את כל התלויות הנדרשות בפייתון, לכן עקוב אחר הוראות ההתקנה לפלטפורמה שלך.
פתח את Ilastik ובחר את זרימת העבודה לניתוח: סיווג פיקסלים, סיווג עצמים, מעקב או ספירת צפיפות. טען את מערך התמונות שלך, שיכול לכלול ערוצים מרובים, תלת-ממד או טיים-לפס.
סמן מספר פיקסלים או עצמים מייצגים בתמונות שלך. מסווג ה-Random Forest של Ilastik ילמד מהסימונים האלו ויחזה אוטומטית תוויות על כל מערך הנתונים.
החל את המודל המאומן לסגמנטציה או סיווג של כל מערך הנתונים. ייצא תוצאות כתמונות מתויגות, מפות הסתברות או טבלאות כמותיות לניתוח והדמיה מתקדמים.
השתמש במצב ללא ממשק גרפי של Ilastik לעיבוד אוטומטי של תמונות מרובות ללא התערבות ידנית, אידיאלי לצנרת ניתוח בקנה מידה גדול.
מגבלות ושיקולים
- תיוג אינטראקטיבי עלול להיות גוזל זמן עבור מערכי נתונים גדולים מאוד
- דיוק תלוי באיכות ובייצוגיות של סימוני המשתמש
- דרישות זיכרון — מערכי נתונים ברזולוציה גבוהה מאוד או בגודל גיגה-בייטים עשויים לדרוש זיכרון RAM משמעותי
- נתונים מורכבים — מסווגי Random Forest עשויים להיות פחות יעילים לעומת רשתות עצביות עמוקות בנתוני דימות משתנים או מורכבים מאוד
שאלות נפוצות
כן, Ilastik תומכת במלואה בנפחים תלת-ממדיים ובניסויי טיים-לפס לסגמנטציה, מעקב וניתוח כמותי לאורך נקודות זמן מרובות.
כן, Ilastik היא תוכנה חינמית וקוד פתוח לחלוטין, זמינה לכל המשתמשים ללא הגבלות רישוי.
לא, Ilastik מספקת ממשק גרפי אינטואיטיבי עם משוב בזמן אמת, מה שהופך אותה לנגישה לחוקרים ללא ידע בתכנות. משתמשים מתקדמים יכולים גם להשתמש בעיבוד אצווה דרך שורת הפקודה.
כן, זרימת העבודה הייעודית למעקב מאפשרת ניתוח תנועת תאים וחלוקתם במערכי נתונים טיים-לפס דו-ממדיים ותלת-ממדיים עם מעקב שושלת אוטומטי.
ניתן לייצא תוצאות סגמנטציה כתמונות מתויגות, מפות הסתברות או טבלאות כמותיות, המאפשרות אינטגרציה חלקה עם כלי ניתוח והדמיה מתקדמים.
כלים אלו מתאימים לרמות מתחילים ועד מומחים. רבים חינמיים וקוד פתוח, ומאפשרים תהליכי עבודה של בינה מלאכותית שניתנים לשחזור ולשיתוף בקהילת המחקר.
אתגרים וכיווני עתיד
אתגרים נוכחיים
מגמות מתפתחות
מודלים בסיסיים של ראייה
מערכות בינה מלאכותית מהדור הבא מבטיחות להפחית את הצורך באימון ספציפי למשימות.
- מודלים כמו SAM ומערכות מבוססות CLIP
- בינה מלאכותית אחת לטיפול במשימות מיקרוסקופיה רבות
- פריסה והתאמה מהירים יותר
מיקרוסקופים עם סיוע בינה מלאכותית
מערכות מיקרוסקופיה אוטונומיות וחכמות הופכות למציאות.
- שליטה בשפה טבעית באמצעות מודלים גדולים של שפה (LLMs)
- לולאות משוב אוטומטיות מלאות
- דמוקרטיזציה של גישה למיקרוסקופיה מתקדמת
מסקנות מרכזיות
- בינה מלאכותית משנה במהירות את עיבוד תמונות המיקרוסקופ עם דיוק ואוטומציה משופרים
- למידה עמוקה עוקפת למידת מכונה מסורתית בתמונות מיקרוסקופ מורכבות ומשתנות
- CNN לומדות אוטומטית תכונות היררכיות מפיקסלים גולמיים לניתוח אמין
- יישומים מרכזיים כוללים סגמנטציה, סיווג, מעקב, הפחתת רעש ורכישה אוטומטית
- הצלחה תלויה באיכות הנתונים ובאימות קפדני על ידי מומחים
- מודלים בסיסיים של ראייה ומיקרוסקופים עם סיוע בינה מלאכותית מייצגים את עתיד התחום
עם התקדמות מתמשכת ומאמצי קהילה (כלים בקוד פתוח, מערכי נתונים משותפים), הבינה המלאכותית תהפוך יותר ויותר לחלק מרכזי מ"עין" המיקרוסקופ, המסייעת למדענים לראות את הבלתי נראה.







No comments yet. Be the first to comment!